免疫微环境影响着肿瘤的演化,既可以预测预后,又可以预测对免疫疗法的反应。然而,对肿瘤浸润淋巴细胞(TIL)的测量由于缺乏适当的数据而受到限制。DNA全外显子组测序(WES)经常被用来计算肿瘤的突变负担和鉴别可靶向的突变。有鉴于此,英国伦敦大学的Nicholas McGranahan等研究人员,使用DNA测序数据来量化T细胞分数和治疗反应。
本文要点
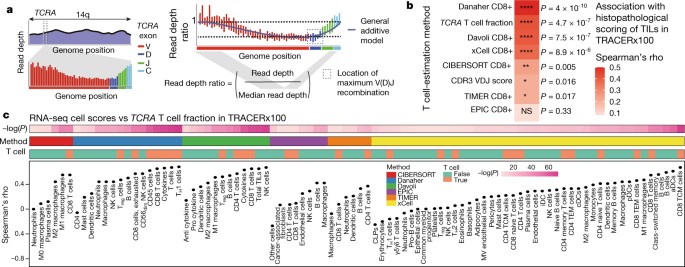
1)研究人员开发了T细胞外显子TREC工具(T cell ExTRECT),这是一种利用T细胞受体-α基因(TCRA,也称为TRA)的V(D)J重组过程中T细胞受体切除圈(TREC)丢失的信号来估计WES样本中T细胞比例的方法。
2)TCRA T细胞分数与正交TIL估计值相关,与样本类型无关。女性的血液TCRA T细胞分数高于男性,并与肿瘤免疫浸润和细菌测序读数的存在相关。肿瘤TCRA T细胞分数在肺腺癌中具有预后作用。
3)通过对接受免疫治疗的肿瘤进行荟萃分析,研究人员发现肿瘤TCRA T细胞分数可以预测免疫治疗的反应,并提供了测量肿瘤突变负担以外的价值。
4)将T细胞ExTRECT应用于一个多样本的泛癌症队列,结果显示出肿瘤内免疫浸润程度的高度多样性。包含SPPL3的12q24.31-32亚克隆缺失与TCRA T细胞分数的减少有关。
本文研究结果表明,T细胞ExTRECT提供了一种成本效益高的技术来描述免疫浸润和体细胞变化的特征。。
参考文献:
Robert Bentham, et al. Using DNA sequencing data to quantify T cell fraction and therapy response. Nature, 2021.
DOI:10.1038/s41586-021-03894-5
https://www.nature.com/articles/s41586-021-03894-5


















